诊断试验是一种常见的meta分析的类型,诊断试验如何使用R语言进行meta分析呢?下面小编带大家实操展示,小伙伴别掉队啦。
使用R语言新版本R version 3.6.1,下载地址https://www.r-project.org/。使用的镜像大陆的镜像,要是发现下载不流畅,选择另一个镜像。注意!镜像选错,就无法下载。
使用新版本的Rstudio,下载地址https://www.rstudio.com/。
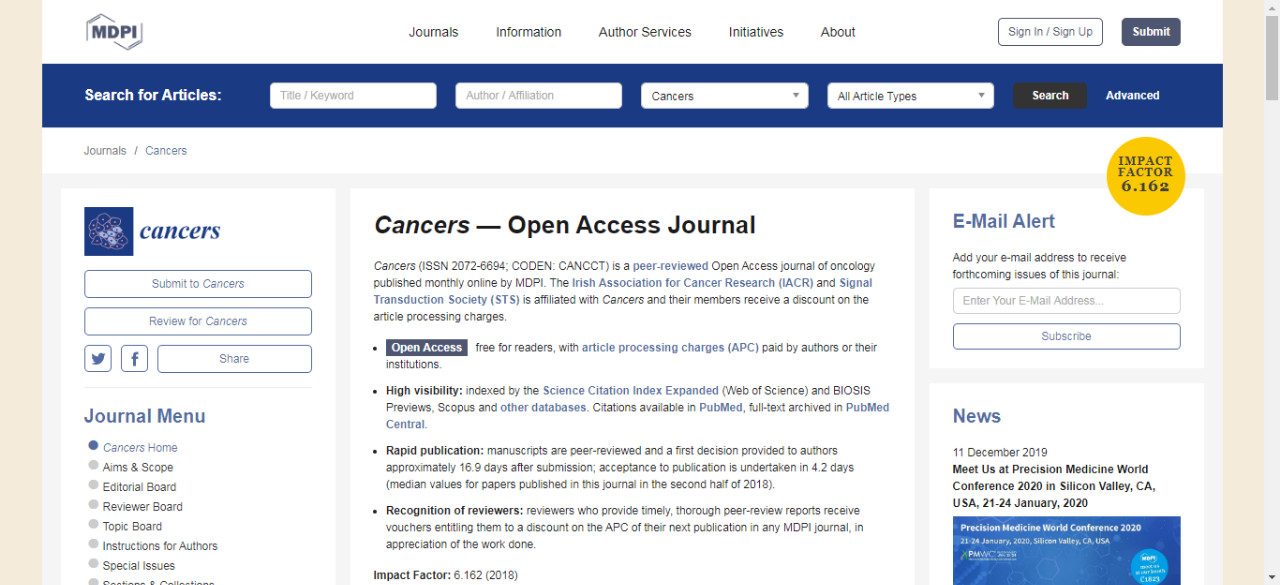
数据库的格式改为.csv格式,使用Excel即可搞定,在Excel保存的格式中选择.csv即可。其实,.xls文件也能在R语言下运行,但是.csv文件更小,在R中运行效果更好,所以要尽量转变为.csv格式。
下面的操作依据这个表格进行。
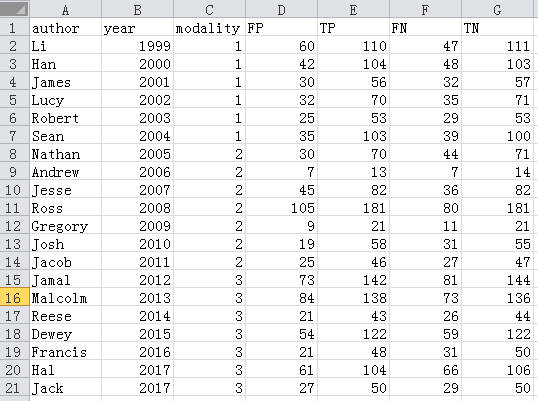
导入数据库,首先将代码读取到R软件中,执行代码。
library(readr)
rate <- read_csv("D:/Scheidler.csv")
也可以进行菜单操作,打开菜单顺序:file-import dateset-fromtest(readr),打开后出现如下图
安装数据包,执行命令install.packages("metamisc"),结果如图

然后安装JAGS,因为metamisc程序包的计算内核是通过JAGS(Just Another Gibbs Sampler)软件3.0及以上版本来实现的,因此使用该程序包时,还需提前在电脑上安装JAGS软件,并同时在R中安装及加载对应的rjags程序包来调用JAGS软件。
JAGS可以通过这个网站下载https://sourceforge.net/projects/mcmc-jags/。直接百度一下也能找到。JAGS软件安装完成后,使用下述命令安装及加载rjgas程序包:install.packages("rjags"),结果如下图所示
library(rjags)
library(metamisc)
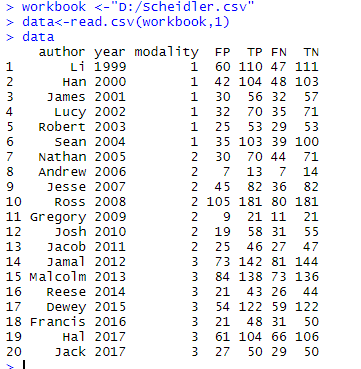
> workbook <-"D:/Scheidler.csv"
> data<-read.csv(workbook,1)
> data
其中workbook,1 指的是工作表的sheet1,显示如下结果
整体结果分析
执行代码
> fit<-riley(data,type="test.accuracy",optimization="Nelder-Mead")
> summary(fit)
代码解读:test.accuracy 为确定该数据为诊断数据;Nelder-Mead为统计方法,结果如下图
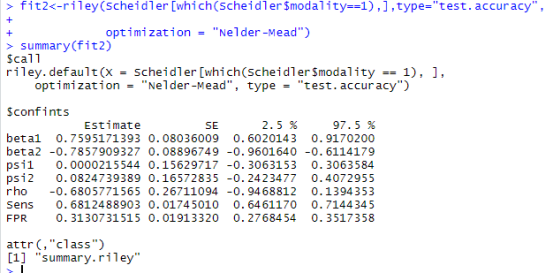
结果解读:Sens是敏感度,FPR是假阳性率,betal是敏感度的logit值,beta2是假阳性率的logit值,psil是betal的抽样误差,psi2是beta2的抽样误差,rho是psil与psi2间的相关性。sens的值就是我们所需要的合并敏感度。
以modality为分亚组依据,首先进行modality=1这一组的分析。
执行命令
>fit2<-riley(Scheidler[which(Scheidler$modality==1),],type="test.accuracy",optimization = "Nelder-Mead")
>summary(fit2)
上述命令中,“modality==1”为分亚组依据;Scheidler[which(Scheidler$modality==1),]代表数据中modality标记为1数据,其余与整体分析中的命令意义一致。
命令运行后的结果如下

第二组、第三组也是相同的方法
绘制图表
使用plot()命令绘制图标
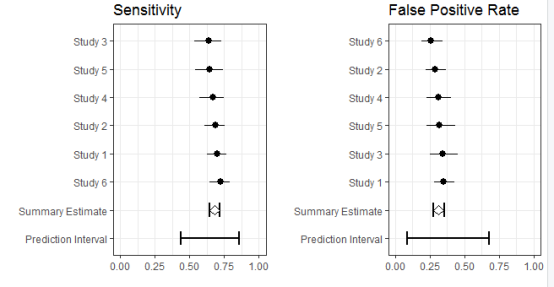
这个是对亚组的作图
执行
> plot(fit2,plotnumerics=FALSE,add=TURE,pch=1)
结果如下图
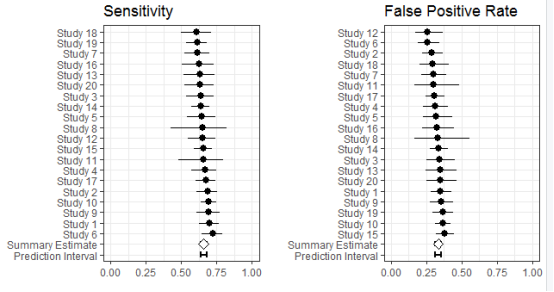
这个是对整体的作图,执行命令
plot(fit,plotsumm=TRUE,plotnumerics=TRUE,CEX.numerics=1)
结果如图
以上就是小编给大家分享的在SCI科研论文写作中如何使用R语言对诊断试验进行meta分析,更多SCI论文写作技巧>>点击咨询<<360期刊网专业论文服务老师。360期刊网专注医学,与进行,拥有500+专业的医学资深编辑,累计,好评率达99.6%!【现在咨询】